Leitura rápida
Rawpixel.com via Shutterstock
Ilustração 3D da bactéria Clostridioides difficile
Por Redação SciAdvances
Fonte
Áreas
Compartilhar
Sob a liderança de pesquisadores do Instituto Karolinska, na Suécia, uma equipe internacional de pesquisadores desenvolveu um método de sequenciamento rápido e econômico capaz de identificar resistência a antibióticos no mesmo dia.
A técnica, chamada s5PSeq, mede a resposta dos ribossomos bacterianos minutos após a exposição a um antibiótico, oferecendo uma leitura molecular do crescimento bacteriano em vez de esperar pelos cultivos tradicionais, que podem demorar dias.
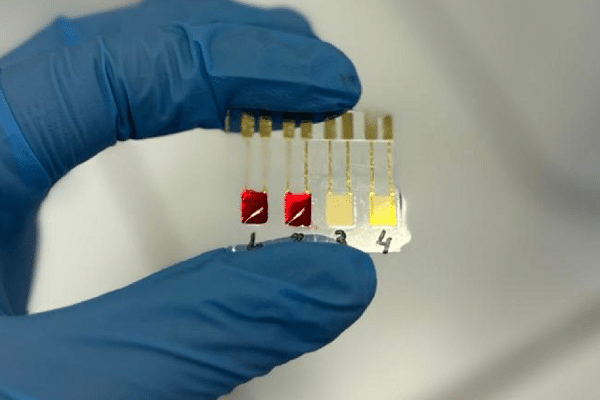
No estudo, publicado na revista científica Cell Reports Methods, os cientistas mostraram que o método consegue distinguir entre cepas de Clostridioides difficile resistentes e cepas sensíveis à eritromicina após apenas dez minutos de aplicação da nova proposta.
Ao detectar padrões característicos no RNA bacteriano, o método pode revelar a suscetibilidade das bactérias muito antes do surgimento de quaisquer diferenças visíveis em seu crescimento.
O Dr. Vicent Pelechano, pesquisador do Instituto Karolinska e autor sênior do estudo, destacou que diagnósticos fenotípicos mais rápidos são essenciais para combater a resistência a antibióticos de forma eficaz, um problema global de saúde pública. O pesquisador ainda ressaltou que, com o novo método, o tempo de espera pelos resultados pode ser reduzido de dias para horas.
Agora, os pesquisadores estão avançando na adaptação do método para testes diretos com amostras complexas de pacientes, sem a necessidade de cultivo prévio das bactérias.
Em colaboração com o Hospital Universitário Karolinska, os pesquisadores também têm a pretensão de expandir o método para outros patógenos e antibióticos, a fim de avaliar seu potencial em contextos clínicos reais.
Publicidade
Autores/Pesquisadores Citados
Instituições Citadas
Publicação
Acesse o artigo científico completo (em inglês).
Publicidade
Outros avanços
Universidade Federal de Alfenas